PATH – Personal Mastery Health & Wellness Data
Laufzeit: 12/2022 – 12/2025
Finanzierungsart: Bundesministerium für Forschung, Technologie und Raumfahrt (BMFTR)
Projektbeschreibung
Das PATH-Projekt zielt darauf ab, das volle Potenzial digitaler Gesundheitsdaten sowohl für die individuelle Versorgung als auch für die Forschung im Bereich der öffentlichen Gesundheit auszuschöpfen. Zu diesem Zweck wird eine DSGVO-konforme, benutzerfreundliche Plattform entwickelt, die persönliche Gesundheitsdaten mit Daten aus Alltagsgeräten wie Smartwatches, Heimtests und Gesundheits-Apps verknüpft.
Im Mittelpunkt des Projekts steht die Schaffung sicherer Infrastrukturen, sogenannter „Datenhubs“, die medizinisch dokumentierten Daten mit selbst erfassten Gesundheitsinformationen integrieren – stets unter der vollständigen Kontrolle des einzelnen Nutzers. Ein grafisches Dashboard bietet den Nutzern einen klaren und leicht zugänglichen Überblick über ihre Gesundheitsdaten und ermöglicht ihnen, selbstständig zu entscheiden, ob und wie ihre Daten weitergegeben werden – sei es zum persönlichen Gesundheitsnutzen (Primärnutzung) oder zu Forschungszwecken (Sekundärnutzung).
Innovation durch digitale Integration
PATH schlägt erstmals eine Brücke zwischen traditionellen klinischen Daten und persönlich generierten Gesundheitsdaten. Diese Integration eröffnet neue Möglichkeiten für:
- Personalisierte Medizin und Vorsorge
- Datengestützte Forschung und Entwicklung neuer medizinischer Produkte
- Überwachung nach Inverkehrbringung zur Bewertung der Sicherheit und Wirksamkeit von Medizinprodukten
Die Plattform ist vollständig DSGVO-konform und bietet Open-Source-Module zur Verwaltung von Einwilligungen, zur Kontrolle der Datennutzung und zur Gewährleistung von Transparenz. Besonderes Augenmerk wird auf eine sinnvolle und nachvollziehbare Einwilligung gelegt, um Vertrauen aufzubauen und eine aktive Beteiligung der Einzelpersonen zu ermöglichen.
Wissenschaftlich fundiert und praktisch erprobt
PATH basiert auf der Hypothese, dass die Bereitschaft zur Weitergabe persönlicher Gesundheitsdaten weitgehend davon abhängt, ob die Betroffenen die Kontrolle behalten und klare, sinnvolle Möglichkeiten zur Verwaltung ihrer Daten erhalten. Um diese Hypothese zu überprüfen, werden die entwickelten Lösungen anhand realer klinischer Fallstudien mit Patienten mit Diabetes und psychischen Erkrankungen validiert.
Die Abteilung für Medical Data Science der Medizinischen Fakultät der Universität Leipzig ist verantwortlich für ein Projektteil und widmet sich der Entwicklung einer digitalen Lösung zur Verwaltung der Einwilligungen.
Ausblick
In einer sich wandelnden Gesundheitslandschaft schafft PATH eine Infrastruktur, die es Einzelpersonen ermöglicht, ihre Gesundheitsdaten sicher, transparent und sinnvoll zu nutzen – zu ihrem eigenen Vorteil und zum Wohle der Allgemeinheit. Das Projekt leistet einen wichtigen Beitrag zur Entwicklung eines europäischen Gesundheitsdatenraums und zur verantwortungsvollen digitalen Transformation der Medizin.
MDS-Projektmitglieder
Projektpartner
- Else Kröner-Fresenius-Zentrum für Digitale Gesundheit (EKFZ) der TU Dresden (Stefanie Brückner, Akrem Dridi, Prof. Dr. Stephen Gilbert, Dr. Cindy Welzel)
- Institut für Internationales Recht, Geistiges Eigentum und Technikrecht der Technischen Universität Dresden (Prof. Dr. Anne Lauber-Rönsberg, Ronja Riedel, Dr. Sven Hetmank)
- Ada Health GmbH, Berlin
- Una Health GmbH
- Movisens GmbH
Ergebnisse
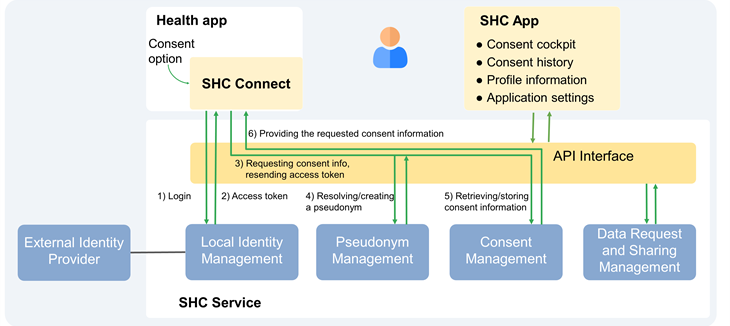
Wir haben zum neuartigen Standard Health Consent (SHC) beigetragen und an dessen Umsetzung gearbeitet, was zu verschiedenen Softwarekomponenten geführt hat. Die folgende Abbildung zeigt die allgemeine Systemarchitektur. SHC Connect ist ein Modul, das in Apps von Drittanbietern integriert werden kann, um app-spezifische Einwilligungen zu erfassen. SHC Connect verweist auf den SHC-Dienst, der alle erfassten Einwilligungsinformationen verwaltet und speichert.
Publikationen
- Welzel C, Ostermann M, Smith HL, Minssen T, Kirsten T, Gilbert S Enabling secure and self determined health data sharing and consent management. npj Digit. Med. 8, 560, 2025. DOI:10.1038/s41746-025-01945-z.
- Brückner S, Kirsten T, Schwarz P, Cotte F, Tsesis M, Gilbert S The Social Contract for Health and Wellness Data Sharing Needs a Trusted Standardized Consent. Mayo Clinic Proceedings: Digital Health 1, 527–533, 2023. DOI:10.1016/j.mcpdig.2023.07.008.